论文解读:机器学习辅助与实时反馈控制 InAs/GaAs 量子点生长
条评论1 论文基本信息
- 标题:Machine-learning-assisted and real-time-feedback-controlled growth of InAs/GaAs quantum dots
- 期刊:Nature Communications 15, 2818 (2024)
- DOI:10.1038/s41467-024-47087-w
- 核心目标:建立分子束外延(MBE)原位表征与材料生长状态之间的实时连接,通过机器学习(ML)取代传统的“试错法”优化量子点(QD)密度。
- 关键词:MBE, Quantum Dots, RHEED, 3D ResNet, Real-time Feedback Control
- 材料体系: InAs/GaAs
- InAs (砷化铟) 与 GaAs (砷化镓):两者均为 III-V 族化合物半导体。
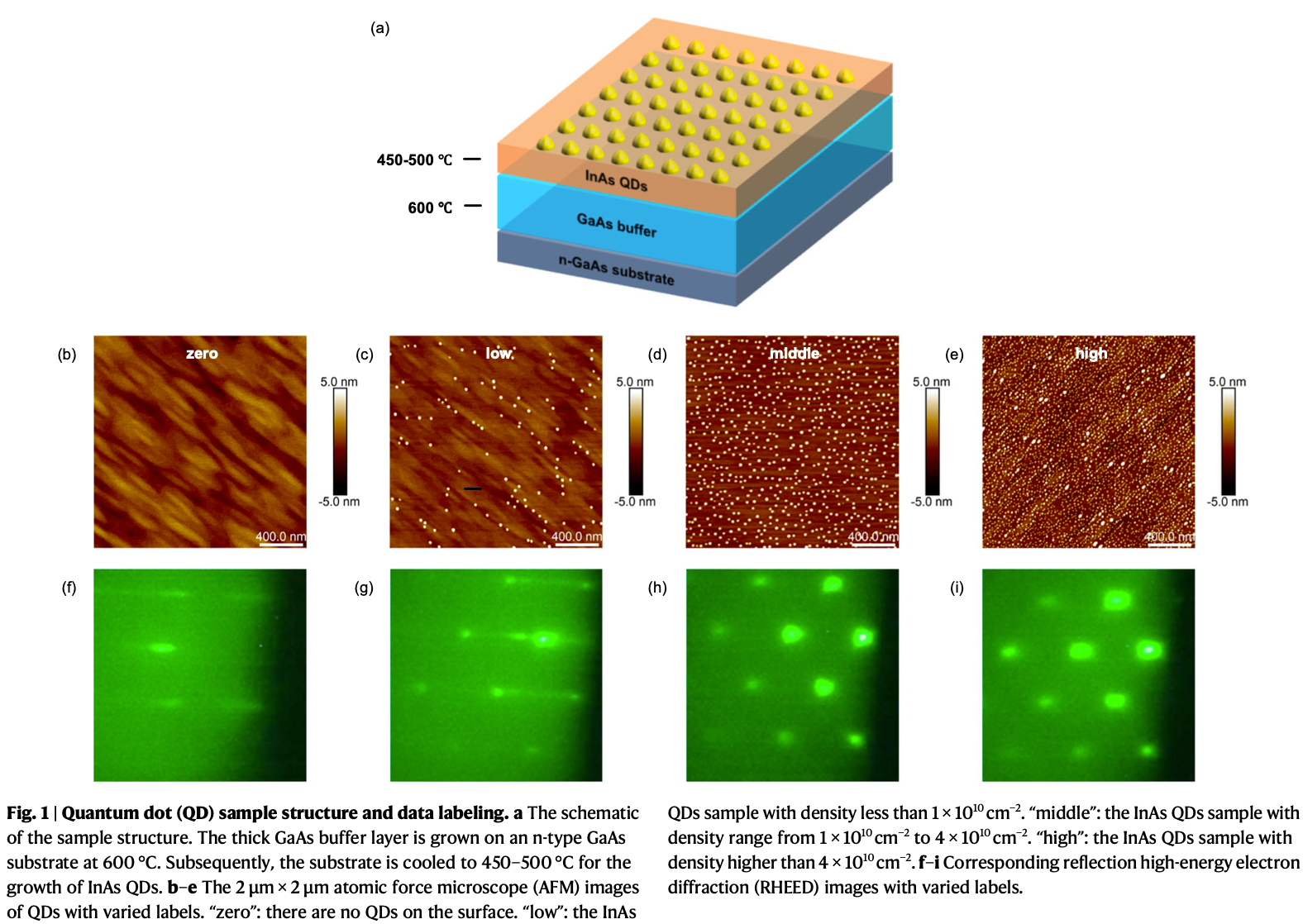
- S-K 生长模式:由于 InAs 与 GaAs 之间存在晶格失配,材料生长会经历从 2D 浸润层到 3D 岛状结构的转变,从而自组装形成量子点。
- 应用驱动:高密度 QDs 适用于量子点激光器,而低密度 QDs(单量子点可寻址)则是单光子源的核心。
2 疑问点
2.1 行业背景:为什么要长这些”点”
光电工程中,半导体量子点(Quantum Dots, QDs)被誉为“人造原子”。
- 核心用途:高密度的量子点适合做量子点激光器,而低密度的量子点则是研制单光子源(量子信息、量子计算关键)的理想材料。
- 生长难题:量子点的生长实在原子层级进行的,通常使用“分子束外延(MBE)”技术,控制原子密度,影响因素有衬底温度、材料比例、生长速率等。
- 现状:过去主要靠资深专家“手感”和不断“试错”,这篇论文的意义在于:用AI取代这种“手感”,实现自动化精准控制。
2.2 实验过程:如何“监控”生长的?
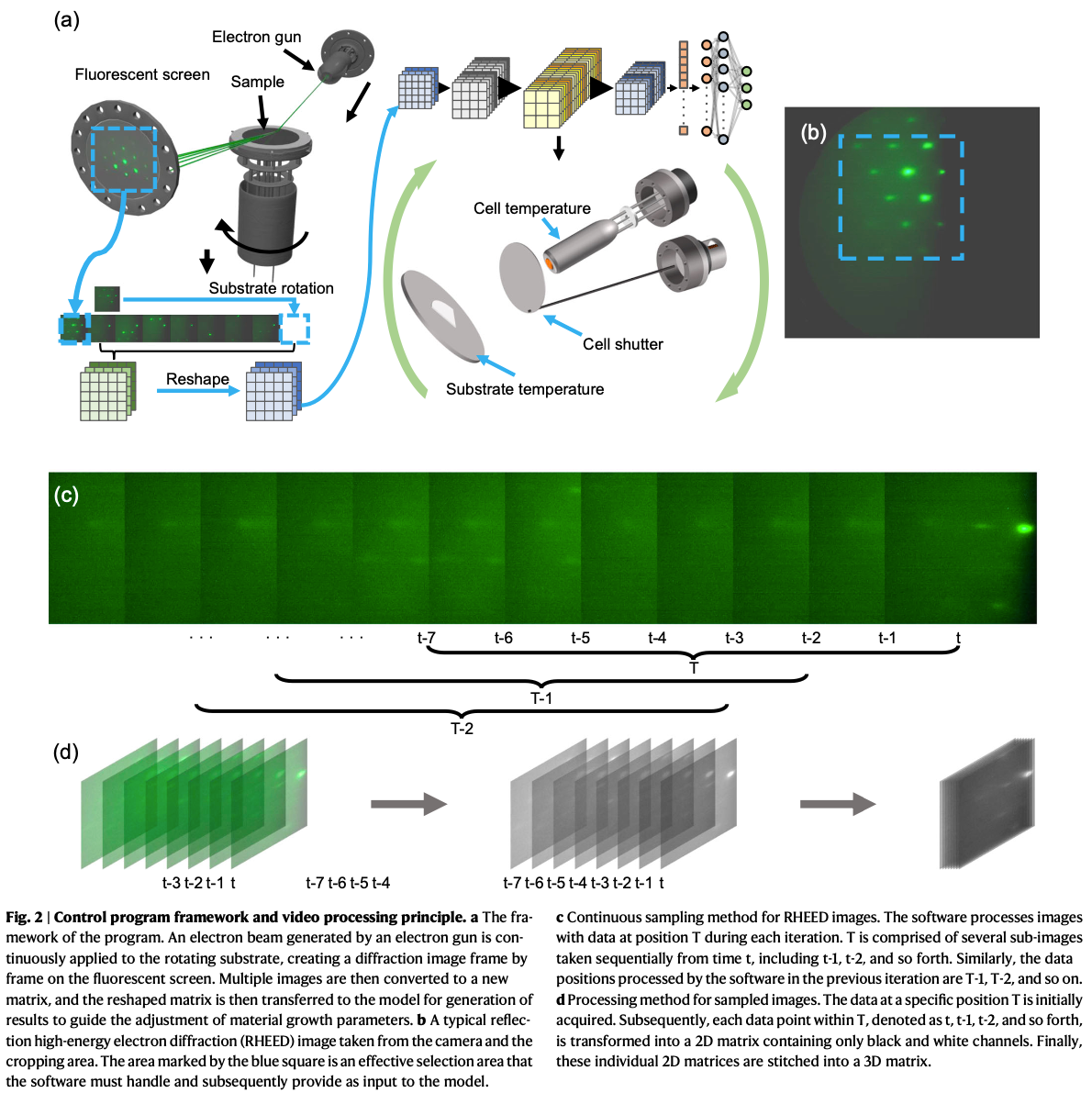
- 数据采集:RHEED技术,在MBE设备里,RHEED(反射高能电子衍射)装置进行采集。
- 原理:向生长中的薄膜表面打一束电子,根据反射回来的衍射图案(亮斑、条纹)来推断表面形貌信息。
- 视觉特征:
- 条纹状(Streaky):对应平整的表面或浸润层阶段 。
- 斑点状(Spotty):对应量子点的成核与形成过程 。
2.3 为什么物理参数固定,仍需要“预测”?
温度、材料比例、生长速率固定为什么结果不同?
计算科学的“确定性”思维,到物理学角度,量子点成核的随机过程。
- 系统的非理想型与参数漂移,MBE机器并不是一个完美的物理模拟器,存在不可忽视的不稳定性和不确定性。
- 传感器误差:即使温度显示500°C,真实腔体内的实际衬底表面温度坑因为加热丝老化、热电偶接触位置的微小变化而发生1-2°C的偏差。
- 束流波动:材料比例依赖于蒸发源的束流强度。随着坩埚内材料的消耗,即便设置同样的加热功率,实际喷射出来的原子流量也会发生微小漂移。
- 预测的必要性:实时预测能检测并纠正这些偏离预期的微小偏差 。
- 物理过程的非线性与复杂性
- 并非简单的函数关系:量子点密度是衬底温度、材料比例、生长速率等大量变量的复杂函数 。
- 难以建模:要建立一个能完美描述这些生长物理过程的综合解析模型是一个极其困难的、甚至无法解决的问题(Intractable problem)
- 实时连接的价值:因为没有完美的公式,所以必须在原位表征(RHEED)与生长状态之间建立实时连接,通过“看”实际长成什么样来反推参数是否合适 。
- 成核过程的随机性,从物理学角度,量子点成核是个随机过程
- 浸润层坍塌:在Stranski-Krastanow(先层状生长再岛状生长)模式下,原子先铺成薄膜,然后突然由于应力坍缩成岛状 。这个“坍缩”的瞬间以及成核的位置具有统计随机性。
- 实时监控意义:AI 预测不是为了验证公式,而是为了捕捉这种随机性中的演变趋势。
- 提高可复用性,传统方法主要依赖研究人员的技能和经验,通过耗时的的“试错法”来寻找参数
- 打破“手感”依赖:即便同一台机器,今天长的和明天长的可能就不一样。
- 自动修正:AI 通过实时预测,可以在生长初期发现“今天的情况似乎往高密度发展了”,从而立即干预(比如升温),确保最终结果能回到目标值,极大地提高了生长的可重复性 。
1 | 把 MBE 生长想象成在狂风中驾驶帆船: |

3 论文解读
3.1 研究核心内容理解
3.1.1 研究背景与挑战
- 传统痛点:在MBE生长过程中,量子点密度的控制是一个多变量优化问题,传统上依赖研究人员的经验和耗时的“试错法”。
- 技术局限:现有的机器学习辅助生长多为“事后”分析,且往往基于静态的反射高能电子衍射(RHEED)图像,未能充分利用生长过程中的时域维度信息。
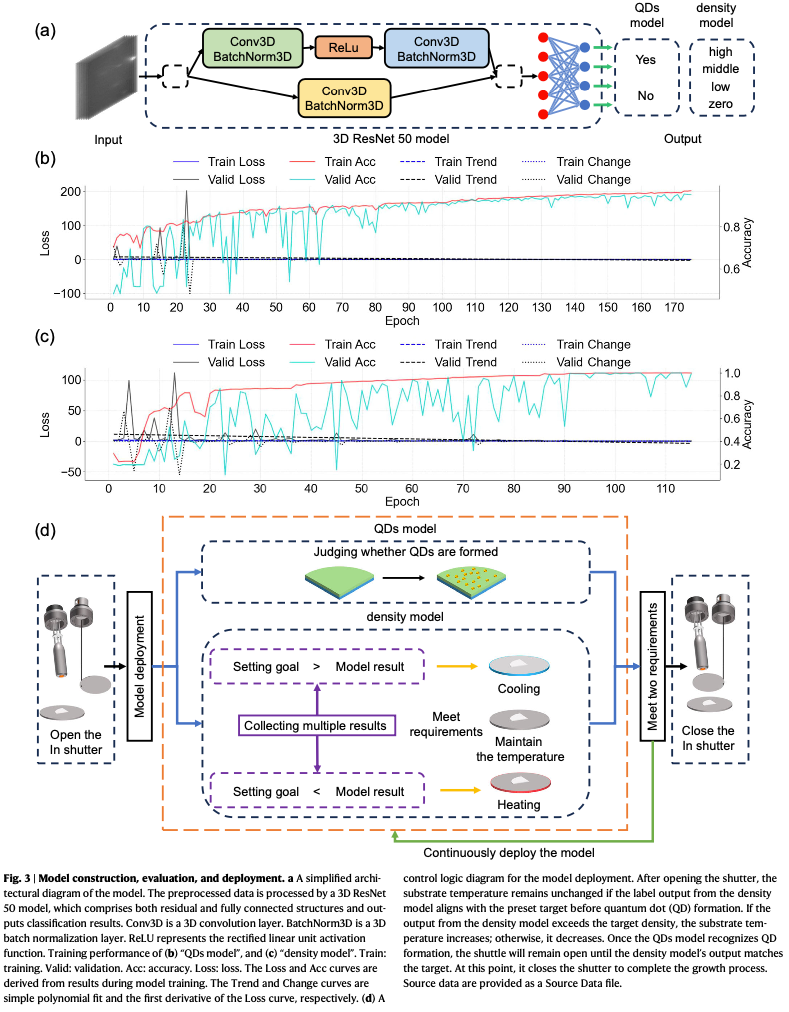
3.2 核心技术方案:3D ResNet 50 模型
研究团队开发并应用了两个结构相同的3D ResNet 50模型,直接以RHEED视频流作为输入:
- 量子点模型(QDs model):实时判定量子点是否已经形成(输出yes or no)
- 密度模型(Density model):将量子点密度分为四个等级:zero、low、middle、high
- 3D卷积优势:将连续的8帧RHEED图像组合成3D矩阵,利用3D卷积提取空间和时间维度信息,比传统的2D CNN更能捕捉视频中的动态特征。
3.3 实时反馈控制逻辑
系统通过LabVIEW程序实现全自动控制,只要分两个阶段:
- 阶段1(形成前介入):在量子点形成前,根据密度模型的预测值实时调节衬底温度。如果预测密度高于目标,则升高温度;反之,则降低温度。
- 阶段2(形成后闭环):一旦量子点模型检测到形成,系统持续监测,直到密度模型输出达到预设目标,立即关闭铟(ln)源快门停止生长。
3.4 主要实验成果与结果
系统成功实现了跨量级密度的精准调控 :
- 模型准确率:量子点形成判定准确率达 94.4%,密度分类准确率达95.1%.
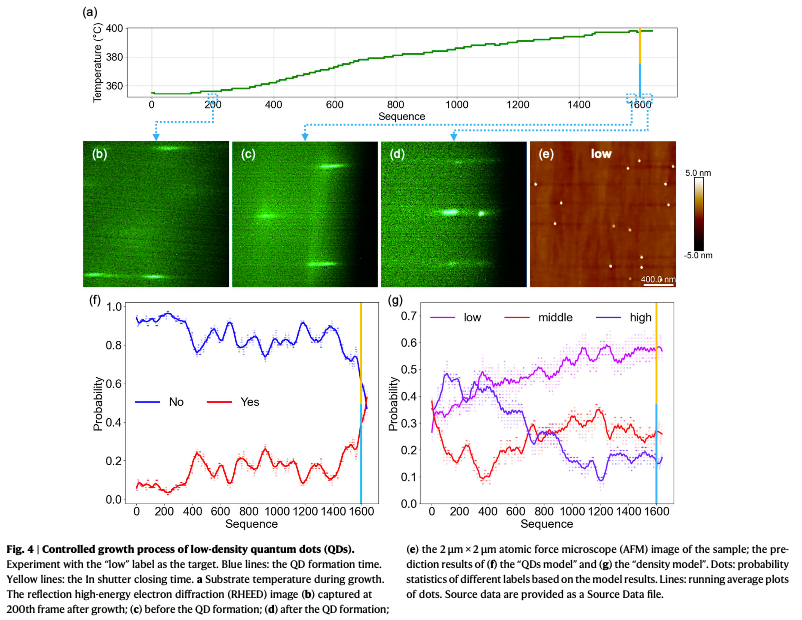
低密度实验 (Fig. 4):以 “low” 为目标,温度从起始位置调升约 $44^{\circ}C$,最终实现 $3.8 \times 10^{8} \mathrm{cm^{-2}}$ 的低密度生长 。 - 高密度实验 (Fig. 5):以 “high” 为目标,温度调降约 $24^{\circ}C$,成功生长出密度为 $1.4 \times 10^{11} \mathrm{cm^{-2}}$ 的量子点 。

4 实验方法
4.1 模型设计
采用 3D ResNet 50 架构,利用 3D 卷积核和批归一化操作提取 RHEED 视频序列中的空间与时间特征 。
4.2 实验流程
4.2.1 数据预处理
- 图像剪裁:从 $1920 \times 1200$ 的原始图像中裁剪出 RHEED 特征区域并压缩至 $300 \times 300$ 。
- 灰度转换与打包:将连续 8 帧图像转换为单通道灰度图并缝合成 3D 矩阵作为输入 。
4.2.2 构建3D ResNet 50模型
- 环境:在 Ubuntu 系统下利用 Python 3.9 和 PyTorch 框架构建, INVIDIA 3090显卡 。
- 特性:相比 2D CNN,该模型能更好地捕捉 RHEED 图案随时间推移的亮度与斑点演化动态 。
4.2.3 训练与增强策略
- 训练集:利用 120 个标记好的 RHEED 视频进行模型迭代 。
- 拟合监控:通过 Valid Trend 和 Valid Change 曲线监控模型收敛性,确保模型稳定捕捉初始状态信息。
4.2.4 推理加速与导出
- 转换:将训练好的模型转换为 ONNX 格式。
- 加速:在 LabVIEW 环境中使用 TensorRT 推理引擎加速,在TensorRT加速下,推理速度约为每秒1个样本,满足实时生长控制需求。(优化毫秒级?)
4.3 实验结果
- 低密度生长:设定目标为 “Low” 时,系统自动将温度调升 $44^{\circ}C$ 以抑制成核,最终获得密度为 $3.8 \times 10^8 \mathrm{cm^{-2}}$ 的样品 。
- 高密度生长:目标为 “High” 时,系统自动降温 $24^{\circ}C$ 以促进成核,最终密度达到 $1.4 \times 10^{11} \mathrm{cm^{-2}}$ 。
- 稳健性:模型能有效适应不同的设备晃动特性(Wobble characteristics) 。
5 结论
- 技术范式转移:该工作实现了从“经验试错”到“实时反馈控制”的转变 。
- 效率提升:显著缩短了工艺参数优化周期,提升了 MBE 生长的可重复性与成品率 。
- 普适性:该方法论具有高度可扩展性,有望推广至多种材料的制备过程,革新半导体制造工业 。
6 衍生研究与创新方向
- 从分类到回归:实现密度的连续数值预测(Fine-grained density regulation),而非四档离散分级 。
- 多目标协同优化:结合量子点尺寸、形状均匀性等多个指标进行综合反馈 。
- 缺陷原位修复:利用此类网络进行早期生长缺陷的检测、识别与自动修复 。
- 多模态感知:集成热成像、质谱等多维度传感器元数据(System metadata),实现更深层次的生长“理解” 。
术语与缩写说明
本文涉及的主要术语与缩写参见 光电、材料与半导体专业术语辞典,统一维护、交叉引用。
参考文献
- Nature Communications 原文:Machine-learning-assisted and real-time-feedback-controlled growth of InAs/GaAs quantum dots
- PubMed 页面:https://pubmed.ncbi.nlm.nih.gov/38553435/